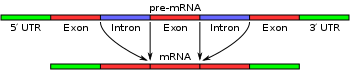
El empalme del ARN es una etapa de la transcripción de los genes. El ARN mensajero (ARNm), que transfiere el código del ADN a las proteínas, se construye en varias etapas coordinadas: iniciación y elongación de la transcripción, modificaciones del extremo 5' (capping), el empalme (splicing) y la poliadenilación del extremo 3'.
En la primera etapa, cada gen se transcribe produciendo un pre-ARNm (también llamado ARN precursor o ARNpre). A continuación, los exones de los ARNpre se unen mediante el empalme, que se realiza en los complejos llamados espliceosomas. El resultado es un ARN mensajero maduro capaz de salir al citoplasma y ser traducido en una proteína funcional.
Qué ocurre durante el empalme
Esto es necesario porque el gen está dividido en secciones codificantes llamadas exones y secciones no codificantes llamadas intrones. Los exones se unen mediante el empalme, y los intrones se eliminan. El proceso se realiza mediante dos reacciones químicas de transesterificación:
- Primera reacción: el adénico de la rama (branch point) ataca el sitio 5' del intrón, formando una estructura en lazo denominada lariat.
- Segunda reacción: el extremo 3' del exón anterior ataca el sitio 3' del intrón, uniendo covalentemente los dos exones y liberando el intrón en forma de lariat, que después se degrada.
El espliceosoma y sus componentes
El espliceosoma es un gran complejo ribonucleoproteico formado por pequeñas ribonucleoproteínas nucleares (snRNPs) y muchas proteínas auxiliares. Las snRNPs más importantes se conocen como U1, U2, U4, U5 y U6; cada una contiene una molécula pequeña de ARN (snRNA) que reconoce secuencias consenso en los extremos de los intrones:
- Sitio 5' (generalmente comienza con GU)
- Punto de ramificación (branch point, con una A conservada)
- Sitio 3' (generalmente termina con AG)
La correcta identificación de estos sitios y el ensamblaje ordenado de las snRNPs permiten la precisión del empalme.
Regulación del empalme y variante funcional
Además del empalme constitutivo (en el que los exones se unen siempre de la misma manera), existe el empalme alternativo, un mecanismo regulado que permite obtener diferentes isoformas de ARNm a partir de un mismo gen. El empalme alternativo es una fuente importante de diversidad proteica en organismos eucariotas: cambia qué exones se incluyen o excluyen, produce variaciones en dominios proteicos, señales de localización o regiones reguladoras.
La selección de sitios de empalme está modulada por:
- Elementos cis en el ARN: enhancers y silencers exónicos o intrónicos.
- Factores trans: proteínas reguladoras como las familias SR (serina/arginina) y hnRNPs, que fomentan o inhiben el uso de determinados sitios de empalme.
- La velocidad de transcripción por la ARN polimerasa II y la estructura de la cromatina, que pueden favorecer empalmes co-transcripcionales.
Consecuencias y relevancia biológica
El empalme correcto es esencial para producir proteínas correctas. Errores en el empalme pueden introducir marcos de lectura erróneos, codones de parada prematuros o eliminar dominios funcionales, y están implicados en numerosas enfermedades genéticas (por ejemplo, algunas formas de beta-talasemia, distrofias y ciertos cánceres). Existen terapias dirigidas a corregir el empalme, como los oligonucleótidos antisentido que modulan la inclusión de exones en casos de enfermedades específicas (por ejemplo, terapias para la atrofia muscular espinal).
Tipos especiales de empalme
- Autoempalme (ribozimas): algunos intrones, como los de tipo I y II en organismos unicelulares y mitocondrias, se excisan sin el espliceosoma porque el propio ARN actúa como ribozima.
- Trans-splicing: fusión de exones procedentes de dos moléculas diferentes de ARN precursor, observado en algunos protistas y nematodos.
Cómo se estudia el empalme
Las técnicas comunes para analizar el empalme incluyen:
- RT-PCR y qPCR para detectar isoformas específicas
- Secuenciación de ARN (RNA-seq) para un panorama global de isoformas y eventos de empalme
- Ensayos CLIP y RIP para identificar interacciones ARN-proteína que regulan el empalme
- Ensayos de reportero para probar efectos de secuencias cis y factores trans en el uso de sitios de empalme
En resumen, en biología molecular, el splicing es un proceso mediante el cual se eliminan los intrones y se unen los exones para obtener el ARNm final. Este ARN mensajero maduro se exporta al citoplasma y se utiliza para producir una proteína correcta mediante la traducción. La regulación del empalme aumenta la complejidad del proteoma y su alteración tiene importantes consecuencias para la salud humana.