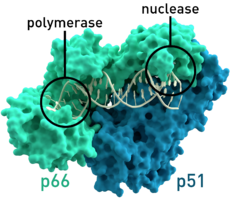
La transcriptasa inversa es una enzima que trabaja "al revés" del ARN al ADN. La transcripción normal implica la síntesis de ARN a partir de ADN; la transcripción inversa es lo contrario. Se trata de una enzima ADN polimerasa que transcribe ARN monocatenario a ADN monocatenario. También sintetiza una segunda cadena de ADN complementaria al ADNc monocatenario transcrito de forma inversa.
Las transcriptasas inversas bien estudiadas incluyen:
- Transcriptasa inversa del VIH-1 (HIV-1 RT): la enzima del virus de la inmunodeficiencia humana tipo 1, ampliamente estudiada por su papel en la replicación viral y como diana de fármacos antirretrovirales.
- Transcriptasa inversa del virus de la leucemia aviar (AMV RT): usada en investigación por su capacidad para sintetizar ADN complementario a partir de ARN.
- Transcriptasa inversa de la leucemia murina (M-MLV RT): otra enzima de uso frecuente en laboratorios para la síntesis de ADNc; existen versiones termoestables y con distinta actividad de RNasa H.
- Telomerasa (TERT): una transcriptasa inversa celular que añade repeticiones teloméricas al extremo 3' de los cromosomas usando un pequeño RNA interno como plantilla (TERC); importante en la senescencia celular y el cáncer.
- Polimerasas de virus como Hepadnaviridae (p. ej. HBV): presentan actividad de transcriptasa inversa integrada en su ciclo de replicación del genoma.
- Transcriptasas inversas de retrotransposones y elementos intergénicos: participan en la movilidad de estos elementos y han contribuido a la evolución genómica.
Mecanismo de acción
La transcriptasa inversa es una RNA‑dependiente ADN polimerasa. Su acción típica en retrovirus sigue pasos generales:
- Un primer (por ejemplo un tRNA viral en retrovirus) se une al ARN molde y proporciona un extremo 3' libre para la elongación.
- La enzima sintetiza el ADN complementario de cadena negativa (ADNc−) usando el ARN como plantilla.
- La actividad RNasa H de la misma proteína (o de una subunidad asociada) degrada el ARN del híbrido ARN:ADN, excepto segmentos necesarios para saltos de plantilla.
- Se sintetiza la segunda cadena de ADN (cadena positiva), resultando en un ADN bicatenario que puede integrarse en el genoma de la célula huésped (en retrovirus) o servir de molde para otras etapas del ciclo viral.
Propiedades bioquímicas y fidelidad
En general, las transcriptasas inversas tienen una fidelidad menor que muchas ADN polimerasas dependientes de ADN porque carecen (o tienen baja) actividad exonucleasa 3'→5' de corrección. Esto produce una tasa de error relativamente alta, lo que facilita la variabilidad genética de virus como el VIH y la aparición rápida de variantes resistentes a fármacos. Algunas transcriptasas inversas poseen actividad RNasa H, que es crítica para procesar los híbridos ARN:ADN durante la síntesis del ADNc.
Funciones biológicas y relevancia evolutiva
Más allá de su papel en la replicación de retrovirus, las transcriptasas inversas intervienen en:
- La transposición de retrotransposones y elementos móviles, que remodelan genomas y han contribuido a la expansión y diversificación genética en muchos organismos.
- La síntesis de ADNc a partir de ARN mensajero en experimentos, permitiendo conservar y estudiar secuencias codificantes sin intrones.
- Los procesos celulares relacionados con la telomerización: la telomerasa mantiene extremos cromosómicos y su regulación está implicada en envejecimiento y oncogénesis.
Importancia clínica
La transcriptasa inversa es una diana fundamental en medicina:
- En infecciones por HIV, inhibidores de la transcriptasa inversa nucleósidos (NRTIs) y no nucleósidos (NNRTIs) bloquean la replicación viral y son componentes clave de la terapia antirretroviral combinada.
- El genoma de hepatitis B emplea una polimerasa con actividad RT; algunos antivirales actúan interfiriendo esa actividad.
- La actividad telomerasa está aumentada en muchas células tumorales; por eso la telomerasa es un blanco potencial en terapias anticancerígenas y un biomarcador en investigación clínica.
Usos en laboratorio e investigación
Las transcriptasas inversas son herramientas indispensables en biología molecular:
- Síntesis de ADNc a partir de ARN para clonar genes, crear bibliotecas de cDNA y estudiar expresión génica.
- Técnicas como RT‑PCR y RT‑qPCR emplean transcriptasa inversa para cuantificar ARN mensajero (p. ej. en diagnóstico viral o análisis de expresión).
- Aplicaciones en secuenciación y caracterización de transcritos (RACE, RNA‑seq prep con etapas de retrotranscripción).
- Existen versiones modificadas de RT (termorresistentes, con RNasa H removida) optimizadas para rendimiento y fidelidad en distintas aplicaciones experimentales.
Historia breve
El descubrimiento de la transcriptasa inversa a finales de los años 60 revolucionó la biología molecular. Howard Temin y David Baltimore describieron independientemente esta actividad y compartieron el Nobel de Fisiología o Medicina en 1975 por trabajos relacionados con la replicación de retrovirus y la enzima responsable.
En resumen, la transcriptasa inversa es una ADN polimerasa que copia ARN en ADN, esencial en ciclos de vida virales (retrovirus, hepadnavirus), en mecanismos celulares como la telomerasa, y de enorme utilidad en investigación y diagnóstico molecular. Su elevada tasa de errores y sus dominios funcionales (síntesis y RNasa H) explican tanto su papel evolutivo como su importancia clínica y biotecnológica.